科技创新进展:Hi-TOM 2.0为基因编辑高通量突变鉴定提供一站式解决方案
近日,我所水稻生物育种全国重点实验室王克剑研究员团队在SCIENCE CHINA Life Sciences期刊发表了题为“Hi-TOM 2.0: an improved platform for high-throughput mutation detection”的研究论文,该文对Hi-TOM平台进行了全面升级,新版本不仅新增了4个不同突变类型鉴定功能和对应批量引物设计模块,还对用户界面进行了优化,为科研工作者提供了更为便捷、高效的一站式突变检测。
随着基因编辑工具的不断升级更新,其应用范围已广泛涵盖基础研究、基因治疗及遗传改良等多个关键领域。然而,基因编辑后的详细突变信息鉴定,因不同编辑工具产生的突变类型各异,不同编辑对象所需的检测精度也不尽相同,往往需要依赖大规模的测序分析。传统的Sanger测序在低频突变、嵌合突变及复杂突变等方面解析能力不足,在处理多倍体、多样本或多位点的突变鉴定时,也受限于高昂的测序成本和分析难度。二代测序技术已成为各类突变检测分析的重要手段,但其复杂的文库构建流程和专业的生物信息学分析要求,一定程度上制约了其在基因编辑突变检测中的广泛应用。为突破这一瓶颈,我所王克剑研究员团队经过深入研究,成功开发了Hi-TOM突变鉴定技术。该技术能够针对基因编辑系统产生的各类突变进行精确量化分析,且以其简洁的实验流程和精准的鉴定结果,赢得了科研界的广泛认可,被众多实验室采纳应用。
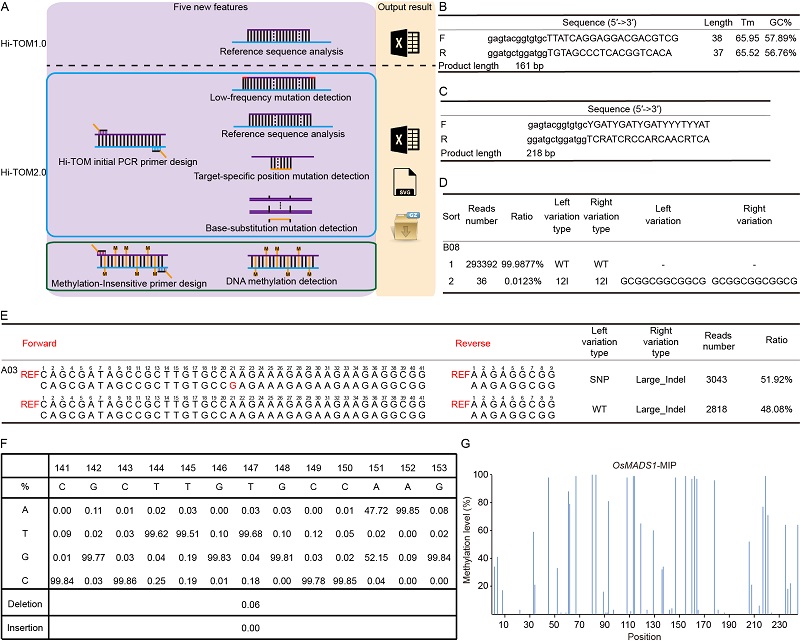
在Hi-TOM 2.0中,为提高批量引物设计效率,新增了Hi-TOM匹配的引物设计流程,其中包含靶序列特异性初始PCR引物和甲基化不敏感引物设计模块,简化了引物设计过程,可批量生成直接适用于后续突变检测的最佳引物。在新增的突变鉴定功能中,首先基于独特的分子标识符(unique molecular identifiers, UMIs),开发了专门针对稀有突变鉴定的低频检测模块,该模块运行不受UMIs的种类以及位置的限制,能够检测频率低至万分之一的稀有突变。其次,提供了靶位点特异区域突变检测模块,该功能可以排除目标区域外突变的干扰,鉴定的突变类型更具有针对性。同时,针对精准碱基编辑技术,增加的碱基替换检测模块,专门用于编辑区域中任意位置碱基替换频率的鉴定分析。此外,结合甲基化不敏感引物设计模块,新版本还开发了位点特异性DNA甲基化建库流程及检测模块,DNA甲基化文库制备仅需要两轮PCR,该功能可以满足表观遗传学研究中对不同区域DNA甲基化水平进行灵活鉴定的需求。Hi-TOM 2.0是一个经过全面优化的突变检测平台,不仅具备丰富的功能分析模块,还拥有强大的批量数据处理能力。它能为用户提供精确、可靠的突变鉴定结果,是科研工作者进行基因编辑研究的得力助手。用户可通过访问http://www.Hi-TOM.net/hitom2/使用该平台。
该研究得到国家自然科学基金等项目资助。我所水稻生物育种全国重点实验室孙亭亭博士后以及刘庆副研究员为该论文共同第一作者,王克剑研究员、刘庆副研究员为文章共同通讯作者。
文章链接:https://doi.org/10.1007/s11427-024-2555-x